import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
from math import sqrt, log, exp0. 정의
Meta analysis: 별도의 연구 결과를 통계적으로 결합하는 과정으로 여러 독립적인 연구 결과를 하나로 통합하는 작업
- 문헌 검토
- 데이터 시트 작성
- 효과 크기 계산
- 메타 분석 결과 해석
1. 문헌 검토
- 연구 질문 정의
- 키워드 식별
- 검색 전략 정의
- 수집된 논문에서 분석 결과 추출
2. 데이터 시트 작성
- 분석 유형
- 여러 연구해서 결론이 내려진 분석 결과를 수식을 통한 계산 작업을 거쳐 표준화된 값으로 변환
- 데이터 유형
- 범주형 유형
- 명목 척도
- 순위 척도
- 연속형 유형
- 등간 척도
- 비율 척도
- 범주형 유형
3. 효과 크기
ttest,anova,correation analysis 등에서 제시된 다양한 연구결과로 아래를 계산
주의할 점은 표본이 작은 경우 효과 크기가 과대추정될 수 있으니 샘플 수를 확인해야 한다는 것
효과 크기
- 표준화된 평균차이
- Cohen
- 두 집단의 비율
- Odds ratio
- 두 변수 간의 상관관계
- Correlation
- 표준화된 평균차이
Cohen’s Effect size: \(d = \frac{\bar{X} - \bar{X}}{S}\)
- <=0.2 작은 효과, 0.2~0.8 중간 효과, >=0.8 큰 효과
연구 결과에서 효과 크기, 신뢰구간, 가중치 해석
- 가중치
- 샘플 수가 달라서 효과 크기 계산에 영향을 줄 수 있어서 조정해줘야 함
- se로
- \(J = (1-\frac{3}{4df-1})\)
- Hedges’ Effect Size = \(g = d\times J\)
이질성 검증
- \(I^2 = \frac{Q-df}{Q} \times 100\)
- 0% ~ 25% 이질성이 낮음
- 25% ~ 75% 중간정도의 이질성이 있음
- 75% ~ 100% 이질성이 높음
- \(I^2\)가 50% 이상이고, 이질성 검증의 유의확률 p-value가 p<0.1인 경우 효과 크기의 이질성이 있는 것으로 판단하고 고정 효과 모델 대신 랜덤 효과 모델 선택
- 랜덤 효과 모델은 더 보수적인 신뢰구간 제공
- 고정 효과 모델 선택하려면 동일한 모딥단에서 추출한 표본의 경우에 사용 가능.
- 일반화 어려움
- 랜덤 표과 모델
- 메타 분석은 다양한 연구를 포함하기 때문에 표본 집단이 다른 경우가 많다.
출판 오류,평향 분석
연구 결과의 신뢰성과 타당성을 보장하기 위함
메타 분석이 실제 효과를 과대 또는 과소 추정할 수 있음
좌우 대칭으로 나오면 편향이 없는 것으로 보지만, 비대칭 분포를 가지면 편향이 있는 것으로 봄
일반적으로 안전계수 값이 \(5 \times N + 10\) 여기서 N은 메타분석 논문수 보다 크면 대체로 안전하다고 판단
4. 실습
첫번째
- Import
- 예제 데이터
- a = treatment effect
- b = treatment non-events
- c = control events
- d = control non-events
df = pd.DataFrame({
"study": ["Study A","Study B","Study C","Study D","Study E","Study F"],
"a": [22, 18, 15, 40, 27, 12],
"b": [78, 82, 75, 160,123, 68],
"c": [30, 25, 24, 50, 35, 11],
"d": [70, 75, 66, 150,115, 69],
})
df| study | a | b | c | d | |
|---|---|---|---|---|---|
| 0 | Study A | 22 | 78 | 30 | 70 |
| 1 | Study B | 18 | 82 | 25 | 75 |
| 2 | Study C | 15 | 75 | 24 | 66 |
| 3 | Study D | 40 | 160 | 50 | 150 |
| 4 | Study E | 27 | 123 | 35 | 115 |
| 5 | Study F | 12 | 68 | 11 | 69 |
- 효과 크기 계산
def log_or_and_se(a,b,c,d, add0_5=True):
if add0_5 and min(a,b,c,d) == 0:
a, b, c, d = a+0.5, b+0.5, c+0.5, d+0.5
logOR = log((a*d)/(b*c))
SE = sqrt(1/a + 1/b + 1/c + 1/d)
return logOR, SEZ = 1.96 # 95% CIdf["logOR"], df["SE"] = zip(*df.apply(lambda r: log_or_and_se(r.a,r.b,r.c,r.d), axis=1))
df["logLCL"] = df["logOR"] - Z*df["SE"]
df["logUCL"] = df["logOR"] + Z*df["SE"]# OR 스케일로 보기
df["OR"] = np.exp(df["logOR"])
df["OR_LCL"]= np.exp(df["logLCL"])
df["OR_UCL"]= np.exp(df["logUCL"])df.round(3)| study | a | b | c | d | logOR | SE | logLCL | logUCL | OR | OR_LCL | OR_UCL | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Study A | 22 | 78 | 30 | 70 | -0.418 | 0.325 | -1.056 | 0.219 | 0.658 | 0.348 | 1.245 |
| 1 | Study B | 18 | 82 | 25 | 75 | -0.418 | 0.348 | -1.100 | 0.264 | 0.659 | 0.333 | 1.303 |
| 2 | Study C | 15 | 75 | 24 | 66 | -0.598 | 0.370 | -1.323 | 0.127 | 0.550 | 0.266 | 1.136 |
| 3 | Study D | 40 | 160 | 50 | 150 | -0.288 | 0.241 | -0.759 | 0.184 | 0.750 | 0.468 | 1.202 |
| 4 | Study E | 27 | 123 | 35 | 115 | -0.327 | 0.287 | -0.890 | 0.236 | 0.721 | 0.411 | 1.266 |
| 5 | Study F | 12 | 68 | 11 | 69 | 0.102 | 0.451 | -0.782 | 0.986 | 1.107 | 0.457 | 2.680 |
- 고정효과 메타분석
w_fixed = 1 / (df["SE"]**2)
theta_fixed = np.sum(w_fixed * df["logOR"]) / np.sum(w_fixed) # 가중 평균
se_fixed = sqrt(1 / np.sum(w_fixed))
fixed_L = theta_fixed - Z*se_fixed
fixed_U = theta_fixed + Z*se_fixed
print("Fixed-effect (log scale):", theta_fixed, "±", se_fixed)
print("Fixed-effect (OR):", exp(theta_fixed),
"(95% CI", exp(fixed_L), "to", exp(fixed_U), ")")Fixed-effect (log scale): -0.34053900893309863 ± 0.12983334833335455
Fixed-effect (OR): 0.7113867755772918 (95% CI 0.551555742161936 to 0.9175339966230908 )- pooled OR 통합오즈비 = 0.71
- 1보다 작다는 건 치료가 더 좋은 효과
- 치료군의 사건 발생 odds가 대조군 대비 약 29% 감소
- 95% CI = 0.55, 0.92
- 95% CI가 1을 포함하지 않음
- 따라서 통계적으로 유의한 차이 존재
- 이질성
Q = np.sum(w_fixed * (df["logOR"] - theta_fixed)**2)
df_Q = len(df) - 1
I2 = max(0.0, (Q - df_Q) / Q) * 100 if Q > 0 else 0.0
print(f"Heterogeneity: Q={Q:.2f}, df={df_Q}, I²={I2:.1f}%")Heterogeneity: Q=1.60, df=5, I²=0.0%- 이질성은 1.60
- \(I^2\)으로 보아 효과 크기 차이가 거의 없음.
- 따라서 모든 연구들이 일관된 방향을 보여줌
- 이질성이 낮으므로 고정효과 모델 결과와 랜덤 표과 모델 결과가 거의 동일하게 나올 것으로 예상
- 랜덤 효과
den = np.sum(w_fixed) - (np.sum(w_fixed**2) / np.sum(w_fixed))
tau2 = max(0.0, (Q - df_Q) / den) # between-study variance (DL)
w_random = 1 / (df["SE"]**2 + tau2)
theta_random = np.sum(w_random * df["logOR"]) / np.sum(w_random)
se_random = sqrt(1 / np.sum(w_random))
random_L = theta_random - Z*se_random
random_U = theta_random + Z*se_random
print("Random-effects (log):", theta_random, "±", se_random, " | tau²=", tau2)
print("Random-effects (OR):", exp(theta_random),
"(95% CI", exp(random_L), "to", exp(random_U), ")")Random-effects (log): -0.34053900893309863 ± 0.12983334833335455 | tau²= 0.0
Random-effects (OR): 0.7113867755772918 (95% CI 0.551555742161936 to 0.9175339966230908 )- \(tau^2\) 값으로 보아 betwee-study variance가 거의 없음
- 따라서 pooled OR이 고정 효과 모델과 동일하게 계산된다.
- 포레스트 플롯
y = np.arange(len(df), 0, -1)
fig, ax = plt.subplots(figsize=(8,7))
ax.errorbar(df["OR"], y,
xerr=[df["OR"]-df["OR_LCL"], df["OR_UCL"]-df["OR"]],
fmt='o', capsize=3)
# 고정/랜덤 풀드 효과(다이아몬드 마커)
ax.plot(np.exp(theta_fixed), 0, marker='D')
ax.hlines(0, np.exp(fixed_L), np.exp(fixed_U))
ax.plot(np.exp(theta_random), -1, marker='D')
ax.hlines(-1, np.exp(random_L), np.exp(random_U))
ax.axvline(1.0, linestyle='--')
ax.set_xscale("log")
ax.set_xlabel("Odds Ratio (log scale)")
ax.set_yticks(list(y) + [0, -1])
ax.set_yticklabels(list(df["study"]) + ["Pooled (Fixed)", "Pooled (Random)"])
ax.set_title("Forest plot: Meta-analysis (OR)")
ax.text(0.02, 0.02, f"Q={Q:.2f}, df={df_Q}, I²={I2:.1f}%, tau²={tau2:.4f}",
transform=ax.transAxes)
plt.tight_layout()
plt.show()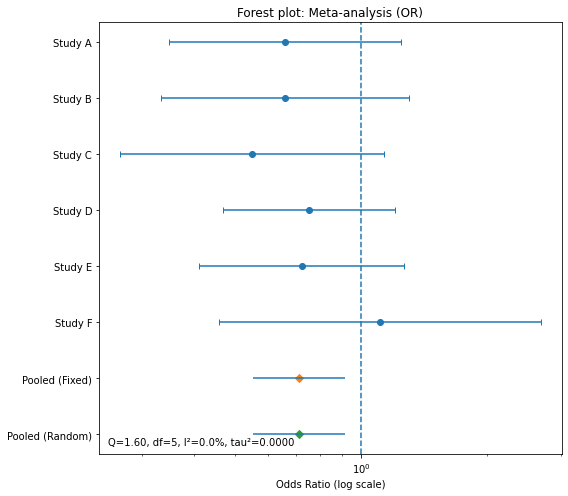
- 대부분의 연구 결과가 왼쪽에 위치, OR <1
- pooled fixed, pooled random이 1보다 왼쪽에 위치
- 전반적인 치료가 효과적임을 시각적으로 확인할 수 있음
두번째
- import
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt- 데이터 연구의 효과 크기, 표준 오차
data = pd.DataFrame({
'study': ['Study1', 'Study2', 'Study3', 'Study4', 'Study5'],
'effect_size': [0.20, 0.35, 0.10, 0.50, 0.40],
'se': [0.10, 0.15, 0.08, 0.12, 0.10]
})data| study | effect_size | se | |
|---|---|---|---|
| 0 | Study1 | 0.20 | 0.10 |
| 1 | Study2 | 0.35 | 0.15 |
| 2 | Study3 | 0.10 | 0.08 |
| 3 | Study4 | 0.50 | 0.12 |
| 4 | Study5 | 0.40 | 0.10 |
- 고정 효과 가중치 계산
\(w_i = \frac{1}{SE_i^2}\)
data['weight_FE'] = 1 / data['se']**2data['weight_FE']0 100.000000
1 44.444444
2 156.250000
3 69.444444
4 100.000000
Name: weight_FE, dtype: float64- 고정효과 모델의 통합 효과 추정
\(\hat{\mu}_{FE} = \frac{\sum w_i y_i}{\sum w_i}\)
- (\(y_i\)): 각 연구의 효과크기
- (\(w_i\)): 각 연구의 가중치
fixed_effect = np.sum(data['weight_FE'] * data['effect_size']) / np.sum(data['weight_FE'])fixed_effect0.2677991137370753- 이질성 검정 Heterogeneity Test
Cochran’s Q
\(Q = \sum w_i (y_i - \hat{\mu}_{FE})^2\)
df = 연구 수 - 1
\(Q \sim \chi^2_{df}\)
data['Q_component'] = data['weight_FE'] * (data['effect_size'] - fixed_effect)**2
Q = np.sum(data['Q_component'])
df = len(data) - 1data['Q_component']0 0.459672
1 0.300310
2 4.399460
3 3.744254
4 1.747707
Name: Q_component, dtype: float64Q10.651403249630723df4\(\chi^2_{0.05} = 9.49\)
- H0 = 이질성이 없다, 모든 연구가 동일하다.
- H1 = 이질성이 있다, 연구가 동일하지 않다.
10.65 > 9.49, 따라서 귀무가설 기각, 이질성이 있다.
- DerSimonian–Laird 추정량, 타우 값 구하기
- 랜덤 효과 모형 추정하기 위해서
랜덤 효과 모형은 \(y_i = \mu + u_i + \epsilon_i\)같은 분포를 따르는 값으로 가정
(\(u_i \sim N(0, \tau^2)\)): 연구 간의 분산(이질성)
(\(\epsilon_i \sim N(0, SE_i^2)\)): 연구 내의 표본 오차
고정효과 모형의 가중치 : \(\frac{1}{s^2}\)
- 이질성 고려 하지 않음
랜덤 효과 가중치 : \(\frac{1}{s^2 + \tau^2}\)
- 이질성 고려는 연구 간 분산인 \(\tau^2\)으로 고려
\(\tau^2 = \frac{Q - (k - 1)}{C}\), 타우가 음수면 0으로 처리
\(C = \sum w_i - \frac{\sum w_i^2}{\sum w_i}\)
C = np.sum(data['weight_FE']) - (np.sum(data['weight_FE']**2) / np.sum(data['weight_FE']))
tau_sq = max(0, (Q - df) / C)C361.20958476940757tau_sq0.018414249040143577- 랜덤 효과 가중치
\(y_i \sim N(\mu, SE_i^2 + \tau^2)\), 각 연구 효과의 분포, 연구내 오차+분산까지 함께 고려
\(w_i^* = \frac{1}{SE_i^2 + \tau^2}\)
data['weight_RE'] = 1 / (data['se']**2 + tau_sq)data['weight_RE'] 0 35.193610
1 24.441363
2 40.299426
3 30.474566
4 35.193610
Name: weight_RE, dtype: float64- 랜덤 효과 모델의 통합 효과 추정
\(\hat{\mu}_{RE} = \frac{\sum w_i^* y_i}{\sum w_i^*}\)
\(SE_{\hat{\mu}_{RE}} = \sqrt{\frac{1}{\sum w_i^*}}\)
random_effect = np.sum(data['weight_RE'] * data['effect_size']) / np.sum(data['weight_RE'])
random_se = np.sqrt(1 / np.sum(data['weight_RE']))random_effect0.29551393503100565random_se0.07770812983895702- 95% 신뢰구간
\(CI = \hat{\mu}*{RE} \pm 1.96 \times SE*{\hat{\mu}_{RE}}\)
ci_low = random_effect - 1.96 * random_se
ci_high = random_effect + 1.96 * random_seci_high;ci_low0.1432060005466499- 결과
print(f"Random-Effects Mean Effect Size: {random_effect:.3f}")
print(f"Between-Study Variance (tau²): {tau_sq:.4f}")
print(f"95% CI: [{ci_low:.3f}, {ci_high:.3f}]")Random-Effects Mean Effect Size: 0.296
Between-Study Variance (tau²): 0.0184
95% CI: [0.143, 0.448]연구 전체 효과는 0.296
타우값으로 보아 이질성은 존재하지만 크지 않음을 보임
신뢰구간이 0을 포함하지 않아 연구 효과가 유의함을 보임
forest plot
plt.errorbar(data['effect_size'], range(len(data)), xerr=data['se']*1.96, fmt='o', color='black')
plt.axvline(random_effect, color='red', linestyle='--', label='Pooled (Random Effects)')
plt.yticks(range(len(data)), data['study'])
plt.xlabel('Effect Size (95% CI)')
plt.title('Forest Plot - Random Effects Meta-Analysis')
plt.legend()
plt.show()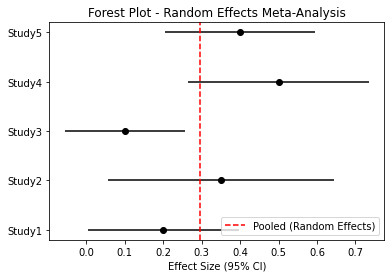
세번째_Fisher’s z 기반 상관계수 변환 분석
- import
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt- data
data = pd.DataFrame({
'study': ['Fonda(2002)', 'Newman(2012)', 'Grant(2003)', 'Granger(2020)', 'Milland(2018)', 'Finch(2021)'],
'r': [0.5, 0.5, 0.4, 0.2, 0.7, 0.45],
'n': [40, 90, 25, 40, 60, 50]
})
data| study | r | n | |
|---|---|---|---|
| 0 | Fonda(2002) | 0.50 | 40 |
| 1 | Newman(2012) | 0.50 | 90 |
| 2 | Grant(2003) | 0.40 | 25 |
| 3 | Granger(2020) | 0.20 | 40 |
| 4 | Milland(2018) | 0.70 | 60 |
| 5 | Finch(2021) | 0.45 | 50 |
- Fisher’s z 변환
- 정규성 확보하기 위해
- r의 분포가 비대칭이라서
- \(z_i = \tfrac{1}{2}\ln\frac{1+r_i}{1-r_i}\)
- \(\mathrm{Var}(z_i) = \frac{1}{n_i-3}\)
- \(SE_i = \sqrt{\frac{1}{n_i-3}}\)
data['z'] = np.arctanh(data['r']) # Fisher’s z
data['var_z'] = 1 / (data['n'] - 3) # 분산(표준오차^2)
data['se_z'] = np.sqrt(data['var_z'])data| study | r | n | z | var_z | se_z | |
|---|---|---|---|---|---|---|
| 0 | Fonda(2002) | 0.50 | 40 | 0.549306 | 0.027027 | 0.164399 |
| 1 | Newman(2012) | 0.50 | 90 | 0.549306 | 0.011494 | 0.107211 |
| 2 | Grant(2003) | 0.40 | 25 | 0.423649 | 0.045455 | 0.213201 |
| 3 | Granger(2020) | 0.20 | 40 | 0.202733 | 0.027027 | 0.164399 |
| 4 | Milland(2018) | 0.70 | 60 | 0.867301 | 0.017544 | 0.132453 |
| 5 | Finch(2021) | 0.45 | 50 | 0.484700 | 0.021277 | 0.145865 |
- 고정효과 가중치
- 모든 연구가 동일한 효과를 추정한다고 가정하는 고정효과
- 각 연구의 신뢰성, 즉 정밀도는 분산의 역수로 가중치를 부여
\(w_i^{FE} = \frac{1}{\mathrm{Var}(z_i)} = n_i - 3\)
data['w_FE'] = 1 / data['var_z']data| study | r | n | z | var_z | se_z | w_FE | |
|---|---|---|---|---|---|---|---|
| 0 | Fonda(2002) | 0.50 | 40 | 0.549306 | 0.027027 | 0.164399 | 37.0 |
| 1 | Newman(2012) | 0.50 | 90 | 0.549306 | 0.011494 | 0.107211 | 87.0 |
| 2 | Grant(2003) | 0.40 | 25 | 0.423649 | 0.045455 | 0.213201 | 22.0 |
| 3 | Granger(2020) | 0.20 | 40 | 0.202733 | 0.027027 | 0.164399 | 37.0 |
| 4 | Milland(2018) | 0.70 | 60 | 0.867301 | 0.017544 | 0.132453 | 57.0 |
| 5 | Finch(2021) | 0.45 | 50 | 0.484700 | 0.021277 | 0.145865 | 47.0 |
- 고정효과 통합 효과 추정치 계산
\(\hat{z}_{FE} = \frac{\sum w_i^{FE} z_i}{\sum w_i^{FE}}\)
z_FE = np.sum(data['w_FE'] * data['z']) / np.sum(data['w_FE'])z_FE0.5475692893176466이질성 체크를 위한 q 통계량
\(Q = \sum w_i^{FE}(z_i - \hat{z}_{FE})^2,\quad df = k-1\)
\(C = \sum w_i^{FE} - \frac{\sum (w_i^{FE})^2}{\sum w_i^{FE}}\)
\(\tau^2 = \max\left(0,\frac{Q - df}{C}\right)\)
Q = np.sum(data['w_FE'] * (data['z'] - z_FE)**2)
df = len(data) - 1
C = np.sum(data['w_FE']) - (np.sum(data['w_FE']**2) / np.sum(data['w_FE']))
tau2 = max(0, (Q - df) / C) # DerSimonian–Laird τ²Q10.750737304131887df5C230.38327526132406tau20.024961609290469623이질성이 낮음, 타우로 보아 이질성이 존재하긴 하는 것으로 보임
- 랜덤 효과 가중치
- 연구 간 효과가 다름을 허용,
- 총 분산을 연구 내 분산과 연구 간 분산의 합으로 사용
\(w_i^{RE} = \frac{1}{\mathrm{Var}(z_i) + \tau^2}\)
data['w_RE'] = 1 / (data['var_z'] + tau2)data| study | r | n | z | var_z | se_z | w_FE | w_RE | |
|---|---|---|---|---|---|---|---|---|
| 0 | Fonda(2002) | 0.50 | 40 | 0.549306 | 0.027027 | 0.164399 | 37.0 | 19.234973 |
| 1 | Newman(2012) | 0.50 | 90 | 0.549306 | 0.011494 | 0.107211 | 87.0 | 27.430431 |
| 2 | Grant(2003) | 0.40 | 25 | 0.423649 | 0.045455 | 0.213201 | 22.0 | 14.201287 |
| 3 | Granger(2020) | 0.20 | 40 | 0.202733 | 0.027027 | 0.164399 | 37.0 | 19.234973 |
| 4 | Milland(2018) | 0.70 | 60 | 0.867301 | 0.017544 | 0.132453 | 57.0 | 23.526384 |
| 5 | Finch(2021) | 0.45 | 50 | 0.484700 | 0.021277 | 0.145865 | 47.0 | 21.627137 |
랜덤 효과 모델의 통합 효과 계산
\(\hat{z}*{RE} = \frac{\sum w_i^{RE} z_i}{\sum w_i^{RE}}\)
\(SE(\hat{z}*{RE}) = \sqrt{\frac{1}{\sum w_i^{RE}}}\)
z_RE = np.sum(data['w_RE'] * data['z']) / np.sum(data['w_RE'])
se_RE = np.sqrt(1 / np.sum(data['w_RE']))z_RE0.5304102438741388se_RE0.08935156116618687- 95% ci
\(CI_z = \hat{z}*{RE} \pm 1.96\times SE*{\hat{z}_{RE}}\)
ci_low_z = z_RE - 1.96 * se_RE
ci_high_z = z_RE + 1.96 * se_REci_high_z0.7055393037598651ci_low_z0.3552811839884126- 상관계수 역변환
- 메타분석 결과를 상관계수로 해석하기 위해서
- 계산은 z로 하고 해석은 r로 함
\(r = \tanh(z) = \frac{e^{2z}-1}{e^{2z}+1}\)
r_RE = np.tanh(z_RE)
r_low = np.tanh(ci_low_z)
r_high = np.tanh(ci_high_z)r_RE0.4856946207056017r_low0.34105082132846415r_high0.6078720252330513- 결과 해석
print("Random-Effects Meta-Analysis (DerSimonian–Laird)")
print(f"Between-study variance (tau²): {tau2:.5f}")
print(f"Pooled Fisher’s z: {z_RE:.4f} (SE = {se_RE:.4f})")
print(f"Pooled correlation (r): {r_RE:.3f}")
print(f"95% CI for r: [{r_low:.3f}, {r_high:.3f}]")Random-Effects Meta-Analysis (DerSimonian–Laird)
Between-study variance (tau²): 0.02496
Pooled Fisher’s z: 0.5304 (SE = 0.0894)
Pooled correlation (r): 0.486
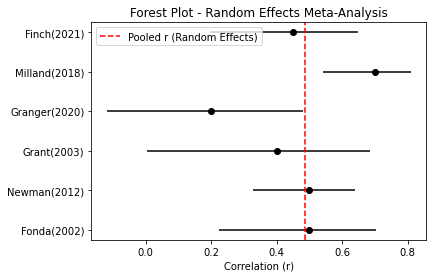
95% CI for r: [0.341, 0.608]- 연구 전반의 상관계수 r은 통계적으로 유의함
- 이질성 타우도 중등도 수준으로 존재함
- 중간 정도 양의 상관관계 r로 해석 가능함
\(z_i \pm 1.96SE_i \Rightarrow r_i^\text{low/high} = \tanh(z_i^\text{low/high})\)
- forest plot에 사용하기 위해서
data['z_low'] = data['z'] - 1.96 * data['se_z']
data['z_high'] = data['z'] + 1.96 * data['se_z']
data['r_low'] = np.tanh(data['z_low'])
data['r_high'] = np.tanh(data['z_high'])data| study | r | n | z | var_z | se_z | w_FE | w_RE | z_low | z_high | r_low | r_high | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Fonda(2002) | 0.50 | 40 | 0.549306 | 0.027027 | 0.164399 | 37.0 | 19.234973 | 0.227084 | 0.871528 | 0.223260 | 0.702150 |
| 1 | Newman(2012) | 0.50 | 90 | 0.549306 | 0.011494 | 0.107211 | 87.0 | 27.430431 | 0.339172 | 0.759440 | 0.326738 | 0.640747 |
| 2 | Grant(2003) | 0.40 | 25 | 0.423649 | 0.045455 | 0.213201 | 22.0 | 14.201287 | 0.005776 | 0.841522 | 0.005775 | 0.686615 |
| 3 | Granger(2020) | 0.20 | 40 | 0.202733 | 0.027027 | 0.164399 | 37.0 | 19.234973 | -0.119489 | 0.524955 | -0.118924 | 0.481515 |
| 4 | Milland(2018) | 0.70 | 60 | 0.867301 | 0.017544 | 0.132453 | 57.0 | 23.526384 | 0.607692 | 1.126909 | 0.542501 | 0.809959 |
| 5 | Finch(2021) | 0.45 | 50 | 0.484700 | 0.021277 | 0.145865 | 47.0 | 21.627137 | 0.198805 | 0.770596 | 0.196227 | 0.647276 |
- 연구 효과의 크기는 검정색 점으로 표시
- 가로선은 각 연구의 95% ci
- 세로 점선은 전체 통합 상관계수 값 r_RE
plt.errorbar(data['r'], range(len(data)),
xerr=[data['r'] - data['r_low'], data['r_high'] - data['r']],
fmt='o', color='black')
plt.axvline(r_RE, color='red', linestyle='--', label='Pooled r (Random Effects)')
plt.yticks(range(len(data)), data['study'])
plt.xlabel('Correlation (r)')
plt.title('Forest Plot - Random Effects Meta-Analysis')
plt.legend()
plt.show()